DISCRIMINAÇÃO DE RAÇAS PRIMITIVAS DE PUPUNHA (zyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBABactris gasipaes) NA AMAZÔNIA BRASILEIRA POR MEIO DE
MARCADORES MOLECULARES (RAPDS)1
Nelcimar R. S O U S A2
, Doriane P. RODRIGUES3
, Charles R. C L E M E N T4 , Eduardo O. NAGAO3
, Spartaco ASTOLFIFILHO3
RESUMOzyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA A pupunha (zyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBABactris gasipaes Kunth, Palmae) foi domesticada por seu fruto pelos primeiros povos da Amazônia Ocidental, possuindo um complexo de raças primitivas (landraces) parcialmente caracterizado e mapeado morfologicamente. Ao longo dos Rios Amazonas e Solimões, no Brasil, foram propostas três raças primitivas [Pará (Rio Amazonas), Solimões (baixo e médio Rio Solimões), Putumayo (alto Rio Solimões)], com indicações de que a raça Solimões poderia ser artefato de análise morfométrica. Marcadores RAPDs foram usados para avaliar a hipótese de três raças. Extraiuse DNA de 30 plantas de cada raça mantida no BAG de Pupunha em Manaus, AM, Brasil. Na amplificação por PCR, 8 primers geraram 80 marcadores, cujas similaridades de Jaccard foram estimadas para agrupamento das plantas com UPGMA. O dendrograma conteve 2 grandes grupos que juntaramse a uma similaridade de 0,535: o grupo da raça Pará conteve 26 plantas dessa raça, 5 da Putumayo e 1 da Solimões; o grupo do Rio Solimões conteve 29 plantas da raça Solimões, 19 da Putumayo e 1 da Pará. A estrutura do segundo grupo sugere que existe apenas uma raça ao longo do Rio Solimões, pois as plantas amostradas são misturadas em subgrupos sem ordem aparente. A análise genética não apoia a hipótese de três raças e sugere que a raça Putumayo estende se ao longo do Rio Solimões até Amazônia central. Será necessário juntar dados genéticos com morfológicos para avaliar esta nova hipótese com mais precisão.
Palavraschave: variabilidade genética, biogeografia, ethnobotânica, análise genética
Discrimination of Pejibaye (Bactris gasipaes) Landraces in Brazilian Amazonia using Molecular Markers (RAPDs)
ABSTRACT The pejibaye (Bactris gasipaes Kunth, Palmae) was domesticated for it fruits by the
first peoples of western Amazonia. Consequently it exhibits a landrace complex that has been partially characterized morphologically and mapped. Along the Amazonas and Solimões Rivers, in Brazil, three landraces have been proposed [Pará (Amazonas River), Solimões (lower and middle
Solimões River), Putumayo (upper Solimões River)], with indications that the Solimões landrace could be an artifact of the morphometric analysis. RAPD markers were used to evaluate the three landrace hypothesis. DNA was extracted from 30 plants of each landrace maintained in the Pejibaye germplasm bank, Manaus, AM, Brazil. During PCR amplification, 8 primers generated 80 markers,
Jaccard similarities were estimated, the plants were grouped with UPGMA. The dendrogram contained 2 large groups that joined at a similarity of 0.535: the group of the Pará landrace contained 26 plants of this race, 5 of the Putumayo and 1 of the Solimões; the group of the Solimões River
contained 29 plants of the Solimões race, 19 of the Putumayo and 1 of the Pará. The structure of the second group suggested that there is only one landrace along the Solimões River, since the plants
were mixed in subgroups without apparent order. This markerbased genetic analysis did not support the three landrace hypothesis and suggests that the Putumayo landrace extends along the Solimões River to central Amazonia. Genetic and morphological data must now be used to evaluate
this new hypothesis.
Keywords: genetic variability, biogeography, ethnobotany, genetic analysis
1
Apoio do Programa Piloto para a Proteção das Florestas Tropicais do Brasil — PP/G7 — Projetos FINEP nº 0930/95 (Embrapa Amazônia Ocidental) e 0869/95 (INPA)
2
Embrapa Amazônia Ocidental, Cx. Postal 319, 69011970 Manaus, AM, Brasil 3
Instituto de Ciências Biológicas, Universidade do Amazonas, 69077000 Manaus, AM, Brasil 4
INTRODUÇÃO zyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA A pupunhazyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA (Bactris gasipaes
Kunth, P a l m a e ) é a m p l a m e n t e d i s t r i b u í d a nos t r ó p i c o s ú m i d o s americanos (Mora Urpí et ai, 1997), e possui ampla diversidade genética nas suas populações cultivadas devido a estas estarem em diferentes estágios de d o m e s t i c a ç ã o e em diferentes a m b i e n t e s . C o m o c o n s e q ü ê n c i a , possui um c o m p l e x o de r a ç a s p r i m i t i v a s q u e foi p a r c i a l m e n t e caracterizado morfologicamente e mapeado (Mora Urpí & Clement, 1988). Estas raças foram criadas pelos p r i m e i r o s povos da Amazônia ao l o n g o de m i l h a r e s de anos de d o m e s t i c a ç ã o p a r t i n d o de b a s e s genéticas diferentes ocorrendo em ambientes diferentes, com o resultado que cada raça possui características morfológicas, químicas e produtivas próprias (Mora Urpí et ai, 1997). T e o r i c a m e n t e , cada raça possui características genéticas diferentes.
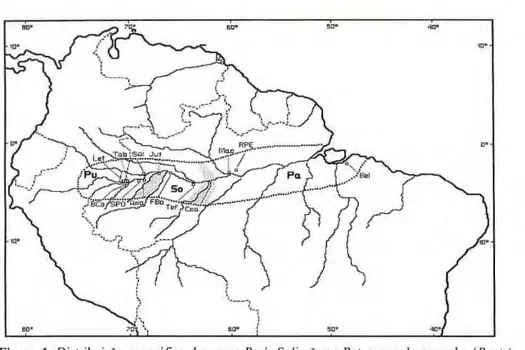
Ao longo dos Rios Amazonas e Solimões, no Brasil, foram propostas três raças p r i m i t i v a s de pupunha (Mora Urpí & Clement, 1988): Pará (Rio Amazonas), Solimões (baixo e médio Rio Solimões) e Putumayo (alto Rio S o l i m õ e s ) (Fig. 1), com i n d i c a ç õ e s que a raça S o l i m õ e s p o d e r i a ser artefato da a n á l i s e m o r f o m é t r i c a ( C l e m e n t , 1986). Portanto, é importante descobrir se as raças propostas com base em análises morfométricas sào geneticamente confirmadas e se a análise genética poderá resolver as dúvidas observadas na análise morfométrica.
A caracterização morfométrica, com base numa lista m í n i m a de descritores para uso in situ e ex situ (Clement, 1986), permitiu a classificação das raças amazônicas de pupunha (Mora Urpí & Clement, 1988). As raças foram identificadas como ' m i c r o c a r p a ' , ' m e s o c a r p a ' e 'macrocarpa' com base no tamanho dos frutos e assumiuse que o tamanho reflete o grau de domesticação da raça. A raça Pará (microcarpa), localizada ao longo do Rio Amazonas (Brasil), possui frutos pequenos, oleosos e fibrosos, e muitos frutos por cacho. A raça Solimões (mesocarpa), localizada ao longo do baixo e médio Rio Solimões (Brasil), possui frutos e cachos intermediários, e é uma das melhores para consumo direto porque sua textura é agradável e contém razoáveis níveis de caroteno e óleo, o que parece contribuir para seu sabor agradável. A raça Putumayo (macrocarpa), localizada ao longo do alto Rio Solimões (Brasil) e áreas adjacentes na Colômbia e Peru, possui frutos grandes, com muito amido e poucos frutos/cacho. Esta raça está começando a fornecer matériaprima para o novo agronegócio de farinha para consumo humano, tanto na Amazônia ocidental como no Acre.
Ill)" 5 0 · 4 0 ·
· 1Π · 1 0 · zyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA
/ P azyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA J 1 .• • • "B e l
c=
/»zyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA ~ / P a J 1 .• • • "
B e l zyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA
{'"·-'.
• 1 0· Λ
V. Ϊ f \ j
/ ί ο · ·
Β ϋ · 5 0 ° Ι Π » /
Figura 1. Distribuição geográfica das raças Pará, Solimões c Putumayo de pupunhazyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA (Bactris gasipaes) na Amazônia brasileira. As populações amostradas foram: Pará Belém (Bel: 5 acessos;
12 plantas), Manaus (Mao: 4 ac; 7 pl), Rio Preto de Eva (RPE: 6 ac; 14 pl); Solimões Coari (Coa: 1 ac; 1 pl), Fonte Boa (FBo: 8 ac; 15 pl), Jutaí (Jut: 2 ac; 5 pl), Tefé (Tef: 4 ac; 9 pl); Putumayo Amaturã (Ama: 2 ac; 5 pl), Benjamin Constant (BCo: 2 ac; 5 pl), Leticia, Colom bia (Let: 2 ac; 4 pl), Santo Antonio do Içá (SAI: 1 ac; 2 pl), São Paulo de Olivença (SPO: 1 ac; 2 pl), Tabatinga (Tab: 6 ac; 12 pl).
Esta sobreposição sugeriu que existe muita introgressão entre estas raças (que é uma suposição lógica devido a sua distribuição linear ao longo destes rios) ou que a raça Solimões é um artefato da análise morfomética (já que a análise discriminante testou uma hipótese de existência do complexo de raças na Amazônia e não apenas ao longo do Solimões/Amazonas). A segunda possível dúvida merece atenção específica porque a hipótese testada com a análise discriminante foi baseada nas impressões visuais de um grupo de
pessoas (MorazyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA Urpí & Clement, 1988), em lugar de estar baseada numa análise
estatística exploratória. Estas dúvidas sobre a raça Solimões podem ser
resolvidas por meio de análises moleculares.
Putumayo) com base na caracterização
molecular por RAPDs. zyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA
MATERIAL Ε MÉTODOS N a A m a z ô n i a b r a s i l e i r a , o Instituto Nacional de Pesquisas da Amazônia mantém o Banco Ativo de Germoplasma de Pupunha (BR 174, km 3 8 , M a n a u s , A M , Brasil), em c o l a b o r a ç ã o com a E m b r a p a R e c u r s o s G e n é t i c o s e E m b r a p a Amazônia Ocidental. O BAG contém 450 acessos coletados de populações cultivadas e 5 de silvestres. Utilizou se 91 plantas de três raças, sendo 30 de c a d a u m a das r a ç a s Pará (+1 planta desta raça, que foi usada em t o d o s os g é i s ) , S o l i m õ e s e P u t u m a y o . A s p l a n t a s f o r a m s e l e c i o n a d a s p a r a r e p r e s e n t a r a d i s t r i b u i ç ã o b r a s i l e i r a da r a ç a Putumayo, a maioria da distribuição da raça Solimões (a parte oriental é mal representada no BAGPupunha e n ã o foi i n c l u í d a ) , e a p a r t e ocidental e oriental da raça Pará (a parte central é mal representada no BAGPupunha, e não foi incluída). A Figura 1 apresenta as populações amostradas e o número de acessos e plantas em cada.
E x t r a i u s e o D N A c o m o DNAsy Plant Minikit da Quiagen, utilizandose 100 mg do meristema apical de um estipe lateral, como
praticado por ClementzyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA et al. (1997) na extração de enzimas, obtendose
em média(±desvio padrão) 72±30 n g d e D N A / m l ( m í n i m o 16; m á x i m o 140 n g / m l ) . Os R A P D s foram obtidos conforme Williams
et al. ( 1 9 9 0 ) : as r e a ç õ e s d e amplificação para volume final de 3 0 :1 c o n t i n h a m 3 m l d e D N A genômico (5 ng/ml), 3 ml de dNTP (2,5 m M ) , 4,2 ml de M g C l2 (25 m M ) , 7 ml do "primer" (10 ng/ml),
1,5 U de enzima "Taq p o l i m e r a s e " (CENBIOT/RS) e 3 ml de Tampão 10X (TrisHCl 200 m M p H = 8 , 6 ; KC1 500 mM). As amostras foram a m p l i f i c a d a s em t e r m o c i c l a d o r (Perkin Elmer 9600) p r o g r a m a d o para 1 etapa de 2 min a 9 42
C , 40 ciclos de 1 min a 9 2 C , 1 min a 3 6e
C e 2 min a 72Q
C, mais 1 etapa d e 3 m i n a 7 2S
C . O s p r i m e r s utilizados foram da Operon Tech nologies (Tab. 1). Os RAPDs fo ram separados em gel de agarose ( 1 , 5 % ) , v i s u a l i z a d o s p o r f l u o r e s c ê n c i a c o m b r o m e t o d e etidio e fotografados para posterior interpretação.
As duas p r i m e i r a s e ú l t i m a s fileiras (plantas) em cada gel foram d e s c a r t a d a s em função da b a i x a qualidade fotográfica nas b o r d a s , sendo considerada na análise 27 p l a n t a s da r a ç a P a r á , 3 0 da S o l i m õ e s e 2 4 d a P u t u m a y o . B a n d a s foram c o d i f i c a d a s como presente ou ausente. As similaridades de Jaccard foram estimadas da matriz binaria; a matriz de similaridades foi usada para gerar um dendrograma com base em UPGMA (Rolf, 1990).
razoável confiança (56 foram descartados por pouca resolução). Destes 80 m a r c a d o r e s , 71 foram polimórficos no conjunto das plantas, mas cada raça apresentou um número diferente e menor que este (Tab. 1).
O dendrograma conteve 2 grandes grupos que se juntaram a uma similaridade de 0,535 (Fig. 2). O grupo da raça Pará conteve 26 plantas dessa raça, 5 da Putumayo e 1 da Solimões. O grupo do Rio Solimões conteve 29 plantas da raça Solimões, 19 da Putumayo e 1 da Pará.
Detectouse quatro possíveis problemas com esta análise: (1) a maior similaridade entre indivíduos dentro dos grupos foi de 0,85, na raça Pará, que é mais distante do que
esperadozyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA a priori; se esperava que i n d i v í d u o s de um m e s m o acesso
(oriundos da mesma matriz) teriam s i m i l a r i d a d e s > 0,90; (2) a
similaridade entre grupos foi muito pequena (0,535), que é uma distância esperada entre espécies e não entre raças dentro de uma espécie; (3) a presença de plantas estranhas em cada grupo, ou seja, que estavam fora do grupo esperado, o que poderia ser erro de plantio, de coleta da amostra ou de m a n i p u l a ç ã o da a m o s t r a no laboratório; cada planta estranha ao seu grupo precisará ser reanalisada futuramente para determinar se foi erro ou realmente é membro de outro g r u p o ; (4) i n d i v í d u o s do m e s m o acesso encontrados em dois ou mais subgrupos, quando se esperava que estes i n d i v í d u o s f o r m a r i a m os subgrupos; esta situação foi observada em Elaeis oleifera também, embora em menor freqüência (E. Barcelos, Embrapa, com. pess.).
O grupo da raça Pará apresentou
TabelazyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA 1. Número de marcadores (RAPDs) úteis obtidos de cada primer (Operon) usado nas
três raças de pupunha (Bactris gasipaes) e número de marcadores polimórficos em cada raça. zyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA
N ° N° P o l i m ó r f i c o s
P r i m e r M a r c a d o r e s T o t a l P a r á S o l i m õ e s P u t u m a y o
O P A - 0 1 5 5 5 3 5
O P A - 0 4 1 0 8 7 8 8
O P A - 0 5 15 12 11 12 12
O P A - 0 8 13 13 11 13 1 2
O P A - 0 9 1 1 10 9 9 9
O P A - 1 8 12 12 11 9 10
O P A - 2 0 9 9 9 9 8
O P A V - 1 5 5 2 2 1 2
S imilaridade de Jaccard
0,50 zyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA
Morforaças Pará Solimões Putumayo
0,60 0,70 0,80
C
0,90
Pa.Mao.019.8 Pa.Mao.019.9 Pa.RPE.034.4 Pa.Bol.059.3 Pa.RPE.037.2 Pa.RPE.259.7 Pa.Mao.269.2 Pa.Mao.297.9 P a . R P E . 0 3 7 J Pa.Mao.270.6 Pa.Mao.270.2 Pu.Tab.048.9 Pa.Bcl.059.5 1 _ P a . B c l . 0 5 9 . 2
Pa.RPE.259.9 Pa.Bcl.060.2 Pa.Bcl. 060.1 Pu.SPO.049.1 Pa.Mao.269.5 Pa.Bcl.049.4 Pa.Bcl.050.5 Pa.Bcl.049.1 Pa.Bcl.050.3 Pa.Bcl.055.2 P a . B c l . 0 5 0 . 3 — P u . A m a . 0 5 2 . 4
P a . B c l . 0 4 9 . 2 P u . S P O . 0 4 9 . 4 Pa.RPE,281.4 Pu.Tab.002.8 S o . T c f . 0 9 8 . 3 P a . R P E 2 8 1 . 9 S o . T c f .044.3 S o . T cf .046.2 S o . F B o . 0 6 8 . 1 So.Jut.071.2 S o . F B o . 0 7 9 . 9 S o . F B o . 0 7 4 . 3 S o . T c f .076.6 S o J u t . 0 6 8 . 8 Pti.Tab.006.9 Pu.Tab.007.9 S o . F B o . 0 8 1 . 5 S o . T c f .07 6.7 S o . F B o . 0 8 1 . 3 P u . B C o . 0 1 6 . 6 So.Jut.071.3 S o . F B o . 0 7 8 . Pu.Tab.006.! Pu.Tab.007,5 S o . F B o . 0 8 l . " Pu.BCo.016.1 Pu.Lct.017.S
Pu.Lct.015.3 P u . B C o . 0 2 6 . ? Pu.Tab.002.7 Pu.Tab.006.1
S o . F B o . 0 7 4 . 4 S o . F B o . 0 7 7 . 6 Pa.RPF..036.2 S o . F B o . 0 7 5 . 3 S o . F B o . 0 6 8 . 9 So.Coa.220.1 P u . B C o . 0 1 6 . 2
ι —
0,50 0,60 0,70 0,80
Similaridade de Jaccard
0,90 zyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA
l
o
6
γ A
Ε
Figura 2. Dendrograma das relações entre plantas de pupunhazyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA (Bactris gasipaes) com base na similaridade de Jaccard estimado da matriz binaria de 80 marcadores RAPDs. Chave:
6 subgrupos e um indivíduo. Os dois primeiros subgrupos (do topo da Fig. 2) representaram Amazônia central, o terceiro representou Amazônia orien tal, com duas plantas estranhas ao grupo, e os outros 3 contiveram pares de plantas com uma própria do grupo e uma estranha ao grupo. O grande número de plantas estranhas neste grupo (19%) pode ser devido aos possíveis erros apontados acima, ou ao fato que já houve muito introdução de germoplasma do alto Rio Solimões (raça Putumayo, especialmente) em Belém e M a n a u s ( M o r a Urpí & C l e m e n t , 1988), o que p o d e r i a influenciar as similaridades.
O g r u p o do Rio S o l i m õ e s a p r e s e n t o u 8 s u b g r u p o s e um i n d i v í d u o . O p r i m e i r o s u b g r u p o r e p r e s e n t o u a r a ç a S o l i m õ e s , os próximos três subgrupos misturaram as raças Solimões e P u t u m a y o , o quinto representou a raça Putumayo, os próximos dois misturaram as raças Solimões e Putumayo, o penúltimo representou a raça Solimões (com uma estranha), e o último subgrupo juntou uma planta do extremo oriental da raça Solimões com uma da raça Putumayo. A ausência de uma estrutura que diferencie a raça Solimões da raça Putumayo sugere que existe apenas uma raça ao longo do Rio Solimões.
Concluise que a análise genética não apoia a hipótese de três raças. Em lugar disto, a análise sugere que a raça Putumayo estendese ao longo do Rio Solimões até Amazônia Central. A raça Pará é apoiada por esta análise, embora
ainda seja necessário determinar seu limite ocidental. Desta forma, será necessário juntar dados genéticos com morfológicos para avaliar esta nova
hipótese com mais precisão. zyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA
Bibliografia citada
Clement, C R . 1986.zyxwvutsrqponmlkjihgfedcbaZYXWVUTSRQPONMLKJIHGFEDCBA Descriptores mínimos para el pejibaye (Bactris gasipaes H.B.K.)
y sus implicaciones filogenéticas. Tese de m e s t r a d o , E s c u e l a de B i o l o g i a , Universidade de Costa Rica, San José, Costa Rica. 216p.
Clement, C.R.; Aradhya, M.K.; Manshardt, R.M. 1997. Allozyme variation in spine less pejibaye (Bactris gasipaes Palmae). Economic Botany, 51 (2): 149157.
F e r r e i r a , Μ . Ε . ; G r a t t a p a g l i a , D. 1 9 9 6 . Introdução ao uso de marcadores moleculares em análise genética. EmbrapaC EN A RG EN, Brasília. 220p.
Mora Urpí, J.; Clement, C R . 1988. Races and populations of peach palm found in the A m a z o n b a s i n . In: C l e m e n t , C . R . ; Coradin, L. (Eds.). Final report (revised): peach palm (Bactris gasipaes H.B.K.) germplasm bank. U.S. A.I.D. project re port. Instituto Nacional de Pesquisas da Amazon ia/Centro Nacional de Recursos Genéticos, Manaus, Amazonas, pp. 7894.
Mora Urpí, J.; Weber, J . C ; Clement, C R . 1997. Peach palm. B a c t r i s g a s i p a e s Kunth. Promoting the conservation and use of underutilized and neglected crops. 20. Institute of Plant Genetics and Crop Plant Research IPK, Gatersleben/Inter national Plant Genetic Resources Institute IPGRI, Rome. 83p.
Rolf, F.J. 1990. NTSYS-pc - Numerical tax-onomy and multivariate analysis system, ver. 1.6. Exeter Software, Setauket, NY.
Williams, J.G.K.; Kubelik, A.R.; Livak, K.J.; Rafalski, J.A.; Tingey, S.V. 1990. DNA polymorphisms amplified by arbitrary p r i m e r s a r e useful g e n e t i c m a r k e r s . Nucleic Acid Research, 18:6531 6535.